RISmedはPubMed検索のためのRのパッケージです。作者はStephanie Kovalchik氏です。ASReview https://asreview.nl/ を用いた文献選定の際には、Title, Abstractのデータを用います。書誌情報と合わせて、これらのデータを含むExcelファイル、またはCSVあるいはRISファイルを用意する必要があります。その際に、RISmedを使うのがひとつの方法です。
PubMedではGETメソッドで直接データベースにアクセスして、検索結果をダウンロードできるe-utilitiesというサービスがあります。MeSHへのAutomatic Term Mappingは適用されません。https://www.ncbi.nlm.nih.gov/books/NBK25501/
それを利用するRのパッケージです。pmSearchも同じサービスを利用しています。
RISmedとtcltk2のパッケージをThe Comprehensive R Archive Network (CRAN)(https://cran.r-project.org/)からRにインストールしておきます。tcltk2は検索結果をCSVファイルとして保存する際のインターフェースとして用います。
Stephanie Kovalchik: RISmed https://cran.r-project.org/web/packages/RISmed/index.html
Philippe Grosjean: tcltk2 https://cran.r-project.org/web/packages/tcltk2/index.html
パッケージがまだインストールされていない場合は、以下のスクリプトをRで実行してください。
#Install the packages.
packneed=c(“RISmed”,”tcltk2″);current=installed.packages();addpack=setdiff(packneed,rownames(current));url=”https://ftp.yz.yamagata-u.ac.jp/pub/cran/”;if(length(addpack)>0){install.packages(addpack,repos=url)};if(length(addpack)==0){print(“Already installed.”)}
以下のRでスクリプトを実行すると検索結果をCSVファイルとして保存できます。SearchWordsと言う変数に検索式search queryを格納しますので、””で囲んであるところを書き換えて使用してください。すべてを選択して、実行すると、ファイル保存のダイアログまで実行されます。ResultsData=EUtilsGet(Results, type=”efetch”, db=”pubmed”)の実行に時間がかかります。
保存したCSVファイルを直接開くのではなく、Excelを起動して、データメニューからテキストまたはCSVファイルからインポートします。元のファイルはUTF-8でエンコードされており、Shift JISがデフォルトのExcelでは文字化けするので、そのような手順を取ります。ファイル保存の際は.xlsxにすることもできます。
また、CSVファイルはテキストファイルなので、Notepad++ https://notepad-plus-plus.org/ などで一度開いて、エンコーディングをUTF-8-BOMに変換するとExcleで直接開いても文字化けしません。
以下にR用のスクリプトを示します。
library(“RISmed”)
library(“tcltk2”)
#Make a search query for PubMed. Write your query in ” “.
SearchWords=”(junior doctor OR young doctor OR resident physician OR intern) AND mindfulness AND humans[mh] AND (english[la] OR japanese[la]) AND hasabstract[tw] AND 2024[dp]”
#Connect and retrieve a list of PubMed IDs. You can change retmax and set years asmindate=2000, maxdate=2024, retmax=2000
Results=EUtilsSummary(SearchWords, type=”esearch”, db=”pubmed”, retmax=2000)
#Show the number of citations retrieved and get title, abstract and other data. This step takes time.
QueryCount(Results)
ResultsData=EUtilsGet(Results, type=”efetch”, db=”pubmed”)
#Make publication year list.
year=YearEntrez(ResultsData)
#Make a list of authors (Last name + initials) for each citation and a list of reference id (first author + year).
au=Author(ResultsData)
refn=length(au)
auv=rep(“”,refn)
refidv=rep(“”,refn)
for(i in 1:refn){
authors=cbind(au[[i]]$LastName,au[[i]]$Initials)
ma=nrow(authors)
authors[1,]
paste(authors[1,1],authors[1,2])
aul=””
for(j in 1:ma){
aut=paste(authors[j,1],authors[j,2])
aul=paste(aul,aut,sep=”, “)
}
aul=substr(aul,3,nchar(aul))
auv[i]=aul
refidv[i]=paste(authors[1,1],authors[1,2],year[i])
}
#Make citation list. No formatting. Including DOI information.
refer=Citations(ResultsData)
cite=rep(“”,refn)
for(i in 1:refn){
cite[i]=refer[[2]][[i]]
}
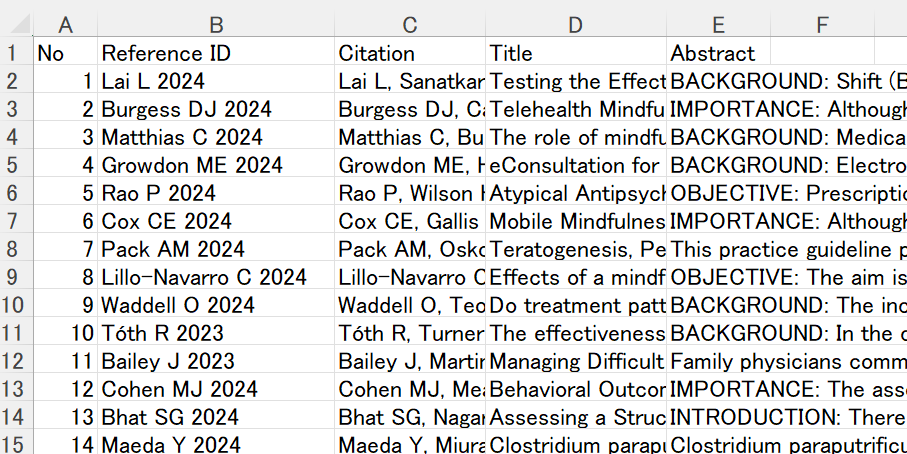
#Create a data frame of PMID, Reference_ID,Citation,Year, Title,Abstract. Citation format is not modified.
pubmed_data=data.frame(‘PMID’=PMID(ResultsData),’Reference_ID’=refidv,’Citation’=cite, ‘Year’=YearEntrez(ResultsData), ‘Title’=ArticleTitle(ResultsData), ‘Abstract’=AbstractText(ResultsData))
#Save the frame work as a CSV file with a save file dialogue. Add file extension “.csv”.
filnam=tclvalue(tkgetSaveFile(initialfile=”export.csv”,filetypes=”{{CSV Files} {.csv}} {{All files} *}”));if(filnam!=”.csv”){write.csv(pubmed_data,filnam,row.names=FALSE)}
#Do not open the file directly to avoid character encoding trouble. Launch Excel, then from Data menu use import text/csv file.
#The saved file is a text file with UTF-8. You can change encoding from UTF-8 to UTF-8-BOM using Notpad++, and you can directly open the file with Excel without garbles.